
科學家開發一種新方法預測蛋白質與環境間的相互作用
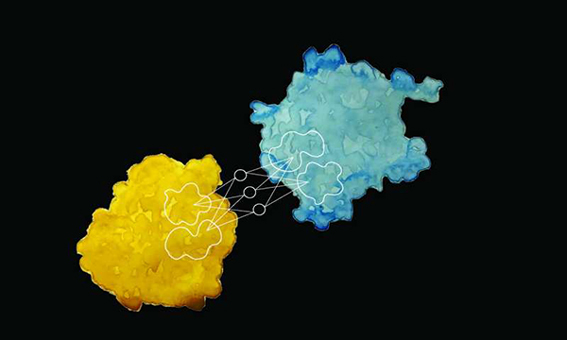
圖片來源:Laura Persat / 2019 EPFL
眾所周知,蛋白質是生命的基石,在所有的生物過程中發揮著關鍵的作用。因此,了解它們如何與環境相互作用,對于開發有效的治療方法和設計人工細胞的基礎至關重要。
近日,由瑞士聯邦理工學院(EPFL)生物工程研究所蛋白質設計與免疫工程實驗室(LPDI)與USI信息學院計算科學研究所、英國帝國理工學院等單位合作,開發了一種突破性的機器學習驅動技術,用于預測蛋白質與環境間的相互作用,并實現僅根據表面描述蛋白質的生化活性。除了加深我們對蛋白質功能的理解,這種被稱為MaSIF的方法還可以支持未來人造細胞中基于蛋白質成分的開發。這項研究已于12月9日發表在Nature Methods上。

在這項新研究中,該研究團隊獲取了大量的蛋白質表面數據,并將這些化學和幾何特性輸入到機器學習算法中,并對其進行訓練,使它們與特定的行為模式和生化活性相匹配。然后,他們使用剩余的數據來測試算法。
該研究第一作者、EPFL生物工程研究所和瑞士生物信息學研究所的Pablo Gainza博士說:“通過掃描蛋白質的表面,我們的方法可以定義一個‘指紋’,然后可以在蛋白質之間進行比較。”
科學家已經開發出一種新的方法來預測蛋白質與其他蛋白質和生物分子間的相互作用,以及僅通過觀察其表面來預測其生化活性。圖片來源:Laura Persat / 2019 EPFL
研究團隊發現,具有類似相互作用的蛋白質都有共同的“指紋”。
研究通訊作者、LPDI主任Bruno Correia博士說:“該算法每秒可以分析數十億個蛋白質表面。我們的研究對人造蛋白質的設計具有重要的意義,它使我們能夠編程讓蛋白質僅通過改變其表面化學和幾何特性就能表現出某種特定的行為方式。”
該方法以開源的形式發表,也可以用來分析其他類型分子的表面結構。
論文鏈接:https://www.nature.com/articles/s41592-019-0666-6


